Analisando coordenadas internas
Coordenadas internas moleculares são conjuntos de comprimentos de ligação, ângulos de ligação e ângulos de torção que definem completamente uma estrutura 3D. As coordenadas internas podem ser usadas em diversas aplicações químicas e investigações de propriedades.
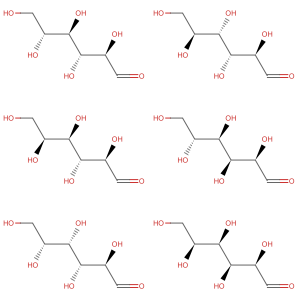
Explore os comprimentos de ligação e os ângulos de torção presentes no dissacarídeo maltose.
Use MoleculeValue para encontrar todos os comprimentos de ligação. A lista de comprimentos de ligações é retornada usando a estrutura eficiente QuantityArray.
Use MeanAround para encontrar o tamanho médio da ligação.
Use BondList para extrair os átomos e comprimentos de cada ligação, agrupe os comprimentos de ligação por átomos membros.
Encontre o comprimento médio da ligação para cada tipo de ligação.
Encontrar ângulos de ligação é mais complexo se cada ângulo envolve duas ligações. Primeiro, defina um padrão representando três átomos quaisquer sequencialmente ligados.
Use FindMoleculeSubstructure para encontrar os índices dos átomos correspondentes a esse padrão.
Para agrupar os ângulos de ligação por tipo de átomo, defina uma função de classificação para garantir que os ângulos CCH e HCC estejam agrupados juntos.
Agrupe as posições de ângulo usando a função angleLabel.
Visualize a variação para diferentes tipos de ângulos de ligação nessa molécula.